
<aside> 🍁 先导编辑器系统(Prime Editor,PE )
Prime editing不会产生DNA双链断裂,不需要供体DNA
Prime editing需要设计一种特殊的gRNA,也就是pegRNA。与普通的gRNA不同,这种pegRNA不但能结合想要进行编辑的特定DNA区域,还自带“修改模板”。
Cas9-逆转录酶融合蛋白会在pegRNA的引导下,精准地切开一条DNA链,然后根据“修改模板”,合成含有正确序列的DNA。细胞内的DNA修复机制会自动把这段新合成的序列整合进基因组。
Prime editing系统由两部分构成
- nCas9 (H840A)与工程化改造的逆转录酶(Reverse Transcriptase, RT)融合构成的效应蛋白
- pegRNA(Prime Editing Guide RNA),包括了single-guide RNA(sgRNA)、引物结合位点(Prime Binding Site,PBS)和储存有靶向位点编辑信息的反转录模板(RT templet with edit)


对Cas蛋白进行了修改,让其只能切断DNA双链中的一条链。另一方面,在向导RNA上接上了一段要添加的DNA的模板RNA**,**成为编辑扩展向导RNA (pegRNA)**,相应的在Cas上加上了一个逆转录酶(利用模板RNA逆转录出来的DNA去修复目标位点)nCas9 (H840A)切口酶在pegRNA上的sgRNA序列指引下,切割DNA单链
为什么一定要在PAM识别链上进行单链切割:因为这样切割后,会在这条单链DNA上形成3′末端(3′ flaps)和5′末端(5′ flaps)两段序列,而5′末端会被具有5'核酸内切酶和5'核酸外切酶活性FEN1和具有5'核酸外切酶活性的EXO1蛋白切割。而3′末端通过反转录酶合成的编辑序列,就可以更大概率的保留在修复后的序列中。通过这套系统,可以在无需引入双链断裂和外源DNA模板的情况下,有效地产生精确的碱基转换或颠换,插入和缺失等变异。
pegRNA 3′-端的PBS(引物结合序列)与切割断点前的互补序列识别配对
逆转录酶(M-MLV RT)以pegRNA上PBS序列后的人工设计的模板序列为模板进行逆转录,将目标序列直接聚合到切口的DNA链上。
反应结束后DNA链的切口处会形成处在动态平衡中的5'-和3'-flap结构,其中3'-flap的DNA链携带有目标突变,而5'-flap结构的DNA链则无任何突变。细胞内5'-flap结构易被结构特异性内切酶识别并切除,之后经DNA连接和修复后靶位点处便实现了精准的基因编辑。
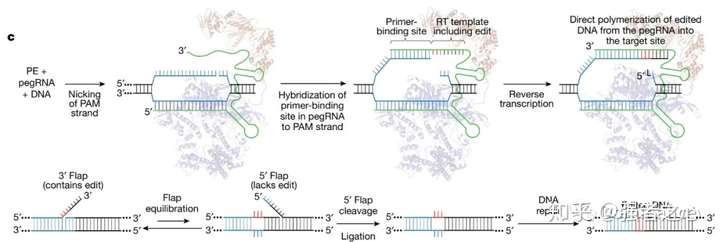
图 PE–pegRNA复合物结合目标DNA位点,并切割含PAM序列的单链
由于PE2编辑后的DNA双链为杂合链,即一条为编辑链,一条为非编辑链。而杂合双链错配修复的模板是随机的,为了解决因错配修复造成的编辑效率降低,他们团队进一步开发出了PE3版本编辑系统,这一版本在非编辑链上距离pegRNA造成的切口处50bp的位置引入了一个新的切口(避免产生双链断裂),从而让细胞尽量多的以编辑链为模板进行DNA修复)。这种方法可以进一步将编辑效率提高1.5-4.2倍,达到55%的编辑率。进一步地,在编辑链修复完成后,再切割非编辑链进行错配修复,理论上可以进一步降低DNA双链断裂的形成和非目标indel的产生。PE3b系统,将切割非编辑链的gRNA 靶向编辑链被编辑后的序列,这样非编辑链上的切口必须要在编辑链被编辑完成后才产生,于是就可以在保留 PE3 编辑效率的同时降低由 DSB修复造成的随机 indel。

图3 PE3系统示意图
